���x�w�W�g�����h�Ɋ�Â��O�������h���̕]��
2011/10/21 �[�V�\��
![]()
0. �͂��߂�
�@�O�������̖h���ɔ������x�w�W[1]�̎��ԕω�����A�h���w�͗ʂƏ������̊W�⎩�R�������𐄒肵�A����ɂ��̐���l��p���č���̏����\�����s��R�X�N���v�g���쐬�����B
�_�E�����[�h
�v���O�����@eradestim1.r
�T���v���f�[�^�@example1.csv
1. ���f���̍\���Ɖ���
1.1. 1�̌̌Q��ΏۂƂ���ꍇ
�@�h���̉e�����Ă���O�������̌̌Q���Ԃ́A���R�����Ə����̃o�����X�ɂ���Č��܂�ƍl������B���Ƃ��A�h���w�͗�[2]���傫����ΊO�������̖��x�͌������邪�A�s�\���ł���ꍇ�ɂ͏����ɂ�錸���������R����������A�O����̑����������~�߂邱�Ƃ��ł��Ȃ����낤(�}�P)�B
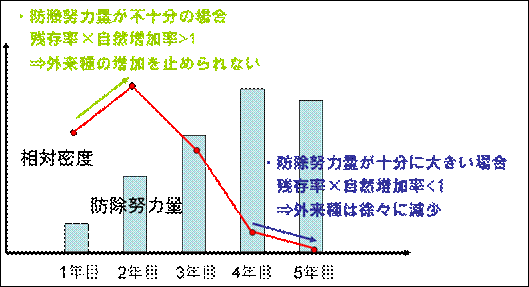
�}�P�@�h���w�͗ʂƌ̖��x�̊W
���̂悤�ȃv���Z�X�́A���̂悤�ȊȒP�Ȍ̌Q���ԃ��f���ŕ\�����Ƃ��ł���B
�����xt = �����xt-1�~�c����t-1�~���R������ (1)
�Ȃ��A�u���Ζ��xt�v�̂悤�ȓY����t�́ut�N�ڂɂ�����l�v���Ӗ�����B�c����t-1�~���R������ < 1�̂Ƃ��Ɍ̖��x�͑O�N�x���猸������(�}1)�B�c�����͖h���w�͗ʂɂ���ĕω����邽�߁A�����ł͈ȉ��̃��f�������肷��B
�c����t = exp(- �h���W���~�h���w�͗�t) (2)
���̎��́A�h���w�͗ʂ�0�̂Ƃ��͎c������1�ŁA�h���w�͗ʂ�������قǎc������0�ɋ߂Â��Ƃ����W�ɑ�������B�h���W��(> 0)���傫���قǁA1�h���w�͗ʂ��̌Q�ɗ^����C���p�N�g���傫���Ȃ�B�Ȃ��A�h���W�����\���������Ƃ��Ɍ���A���̒l�͋ߎ��I�Ɂu1�h���w�͗ʂ𓊓������Ƃ��̏�����(= 1 – �c����)�v�Ƃ��Ă݂Ȃ����Ƃ��ł���[3]�B��(1)��(2)���P�ɂ܂Ƃ߂�ƁA���̂悤�Ȏ���������B
���Ζ��xt = ���Ζ��xt-1�~exp(- �h���W���~�h���w�͗�t-1)�~���R������
�h���W���A���R�������A�����ď�����Ԃɂ����鑊�Ζ��x�����܂�A�h���w�͗ʂɑ��閈�N�̑��Ζ��x���\���ł���B
�@���x�w�W�͑��Ζ��x�ɔ�Ⴗ��l�ł���B�����ł͒P�����̂��߂����̔��W����1�ł���Ƃ���B���x�w�W = ������ / �����w�͗ʂł��鎖����A���L�̊W�����藧�B
���x�w�W�̕���t = ���ϔ�����t / �����w�͗�t = ���Ζ��xt
�� ���ϔ�����t = ���Ζ��xt�~�����w�͗�t
�������̓J�E���g�f�[�^�ł��邽�߁A����2�����z�ɂ����������Ƃ����肷��B
�@��L���܂Ƃ߂�ƁA���L�̂R�̎�����Ȃ�\����������������B
���Ζ��xt = ���Ζ��xt-1�~exp(- �h���W���~�h���w�͗�t-1)�~���R������ (3a)
���ϔ�����t = ���Ζ��xt�~�����w�͗�t (3b)
������t ~ Negative-Binomial(���ϔ�����t, ���U�p�����[�^) (3c)
���R�������A�h���W���A���U�p�����[�^�A�������Ζ��x�̃p�����[�^����͍Ŗޖ@�ɂ��s�������ł���B
�Ȃ��A���f���ɂ͉��L�̉��肪�܂܂�鎖�ɗ��ӂ��ׂ��ł���B
�E ���R�������͎��Ԃɂ�炸���A���x���ʂ͖����ł���قǏ�����
�E �h�������͖��x�ɂ�炸���
�������肵�����Ώۂɏ�L������ł��Ȃ��ꍇ�A����R�[�h�ɂ��Ŗސ��肩�A��ʉ���ԋ�ԃ��f���Ȃǂ̂��������ꂽ��@���g�����Ƃ��������߂������B
1.2. �����̌̌Q��ΏۂƂ���ꍇ
�قȂ�h�������镡���̃T�u�̌Q�̎��ԕω��������Ă���ꍇ�A��(3a)�`(3c)�ɃT�u�̌Q�̃C���f�b�N�Xi��t�����邱�Ƃœ����悤�Ƀp�����[�^���肪�\�ł���B�������A�T�u�̌Q�Ԃ̈ڏo���͖����ł���Ɖ��肷��B
���Ζ��xit = ���Ζ��xit-1�~exp(- �h���W���~�h���w�͗�it-1)�~���R������ (4a)
���ϔ�����it = ���Ζ��xit�~�����w�͗�it (4b)
������it~Negative-Binomial(���ϔ�����it, ���U�p�����[�^) (4c)
������Ԃ̑��Ζ��x�̓T�u�̌Q�̌����݂��鎖�ɂȂ�A�h���W���A���R�������A���U�p�����[�^�ƂƂ��ɂ��ׂčŖސ��肷�鎖�ɂȂ�B
2. �g����
2.1. �f�[�^�̏���
�@�gexample1.csv�h���ɉ������B���̃f�[�^�́A���ȁu�����哇�ɂ�����W�����}���O�[�X�h�����Ɓv�ɂ�����2001-2010�N�x�܂ł̖h���L�^�ł���[4](�����̂�Ȃ��v�[�������f�[�^)�B
|
occasion |
site |
nobs |
surveyeffort |
removeeffort |
|
1 |
1 |
3375 |
165367 |
165367 |
|
2 |
1 |
2191 |
147353 |
147353 |
|
3 |
1 |
2565 |
221403 |
221403 |
|
4 |
1 |
2524 |
318359 |
318359 |
|
5 |
1 |
2591 |
630822 |
630822 |
|
6 |
1 |
2713 |
1051026 |
1051026 |
|
7 |
1 |
783 |
1380751 |
1380751 |
|
8 |
1 |
945 |
1899238 |
1899238 |
|
9 |
1 |
598 |
2174339 |
2174339 |
|
10 |
1 |
311 |
2101116 |
2101116 |
��͂ɍۂ��ẮA���L�̂悤��5��̃f�[�^�Z�b�g��csv�t�@�C���ō쐬����K�v������B
�e��̈Ӗ��͉��L�̂Ƃ���ł���B
occasion������ԃX�e�b�v(�N�A���ȂǁB�ŏ��̃X�e�b�v��1�Ƃ���)
site����T�u�̌Q�̃C���f�b�N�X
�����̃T�u�̌Q������ꍇ�A1���珇�ɔԍ�������B
nobs������j�^�����O�ɂ����錟�o�̐�
surveyeffort������j�^�����O�w�͗�
removeeffort��������w�͗�
��L�̗�ł͂�Ȃɂ��h�����s���Ă���ACPUE�𖧓x�w�W�Ƃ��Ă��邽�߁A���j�^�����O�w�͗� = �����w�͗ʂƂȂ��Ă���B
2.2. R�̃C���X�g�[��
CRAN(http://cran.r-project.org/)�̃~���[�T�C�g����R���_�E�����[�h���A�C���X�g�[������BR�̊�{�I�Ȏg�����ɂ��Ă͋��ȏ���Web�T�C�g�ɏ�W�ς���Ă��邽�߂�������Q�Ƃ��ꂽ���B
2.3. �\�[�X�t�@�C���̓ǂݍ���
R���N��������A���L�̃R�[�h�ɂ�萄��ɕK�v�Ȋ��Q���܂�R�X�N���v�g�heradestim1.r�h��ǂݍ��ށB
source(�g�p�X��/eradestim1.r�h)
�Ȃ��A���l�̏����́A���j���[�o�[[�t�@�C��]��[�X�N���v�g���J���c]�ɂ���Ă��\�ł���B�\�[�X�t�@�C�����e�L�X�g�G�f�B�^�ȂǂŊJ���ƁA���ꂼ��̊��̈�����Ԃ�l�̈Ӗ����Q�Ƃ��鎖���ł���B
2.4. �p�����[�^����
���L��R�R�[�h�ɂ��A����v�Z�A�v�v�ʂ̌v�Z�A�����w�͗ʂƎc�����̐}�����\�ł���B�ȉ��̃R�[�h��R�ɃR�s�[�y�[�X�g���邱�ƂŎ��s���鎖���ł���B
#�f�[�^�̓ǂݍ��� example<-read.csv("�p�X��/example1.csv") #�p�����[�^���� res1<-estim.pd(data=example,noc=10,nsite=1) #noc�͎��ԃX�e�b�v���Ansite�̓T�u�̌Q�� #�Ԃ�l�̏ڍׂɂ��Ă��heradestim1.r�h�̃R�����g�s���Q�ƁB #(.r�t�@�C�����e�L�X�g�G�f�B�^�ŊJ����) #�v�v�ʂ̏o�� summary.pd(res1) #�ߊl�w�͗ʂƕߊl���̊W removalrate.pd(res1)
�� �����I�Ȏ��R������������ł��Ȃ��ꍇ
����̌��ʁA���R�������������I�łȂ��l���Ƃ鎖������B����́A�ߊl�w�͗ʂ̂�����������A���R�����̌��ʂƕߊl�̌��ʂ����܂������ł��Ȃ��ꍇ�ɂ悭�N����B�}���O�[�X�̗�ɂ����Ă����肳�ꂽ���R��������1�����ł���A���̂��Ƃ͎��R�Ɍ̖��x���������Ă��܂����Ƃɑ������A���R�Ȃ��炱��͔��I�Ȍ��ʂł���B���̂悤�ȏꍇ�́A���R�����������O�̒m�����猈�肵�A����ȊO�̃p�����[�^���f�[�^���琄�肷��̂����P�̍�ƂȂ邾�낤�B�������A���R�������̒l�ɑ��Ėh���W���͕q���ł��邱�Ƃ����邽�߁A�����I�Ȕ͈͂Ŏ��R�������̒l�����ʂ肩�����ĉ��̔����������K�v������B
#�p�����[�^���� res2<-estim.pd(data=example,noc=10,nsite=1, fixr=1.43) #fixr�͎��O�Ɏ��R�����������߂�ۂɎw�肷������B�����ł�1.43�Ƃ���
���R���������f�[�^���琄�肷��ɂ́A�ꏊ�܂��͎��Ԃ��Ƃ̕ߊl�w�͗ʂ̂����傫���Ƃ�K�v������B�ŏ��̈����Ԃ͖h�������Ƀ��j�^�����O�݂̂��s�����Ƃ�h�����������Ȃ��ΏƋ��ݒ肷�邱�Ƃ́A�p�����[�^�����͗L���ł���B
2.5. �����\��
�h���̏����\���̂��߂̊��Ƃ��āA�@�̐��Ɋւ��郂���e�J�����V�~�����[�V�����A�A�����̑��Ζ��x��1�Ƃ����Ƃ��̑��Ζ��x�̎��ԕω��̌v�Z�A��2��p�ӂ����B�O�҂͊�̐�Ń��X�N�]���ɂ��p�����鑶���\������(PVA)�ł���A�p�����[�^�Z�b�g����єN���Ƃ̗��N�̕��ό̐���
�̐�t = �̐�t-1�~exp(- �h���W���~�h���w�͗�t-1)�~���R������
�ɂ��v�Z����A���ۂ̌̐��̓|�A�\�����z�ɏ]���Ă���Ɖ��肵�Ă���B��҂͕��ϓI�ȑ��Ζ��x�̎��ԕω����v�Z����݂̂ł���A�N���Ƃ̂���͔������Ȃ��B�R�[�h�̗�����L�Ɏ����B
##10�N�Ԃ̗\�� #10�N��܂ł̖h���w�͗� effort1<-rep(2174339,10) #10�N�Ԃ̌̐��V�~�����[�V���� #(100�����A�����̐���300-1500�̈�l�����Ō���) npred1<-pred.nind(res2$fixr,exp(res2$result$par[1]),effort1,10, nind.init=round(runif(100,300,1500))) #10�N�Ԃ̑��Ζ��x�v�Z rdpred1<-pred.rdens(res2$fixr,exp(res2$result$par[1]),effort1,10)
�̐��̏������ꍇ�̓����e�J�����V�~�����[�V������p���邱�Ƃɂ����ҍ���N�����v�Z�ł���B�����łȂ��ꍇ�͊댯����������ő��Ζ��x��臒l��ݒ肵�A��pred.rdens�ɂ���\������鑊�Ζ��x�����������������_��X�I�ɍ���B���Ƃ݂Ȃ��̂������I�Ǝv����B